Project description
Our innovative project “Quarry biodiversity in focus – exploring the barcode of life” harnessed the power of DNA technology as analysis and science education tool to assess, with molecular resolution, the biodiversity in HeidelbergCement’s restored quarry in Nussloch, Germany.
To address the project’s research question, we established a unique collaboration between science educators of the European Learning Laboratory for the Life Sciences (ELLS) at the European Molecular Biology Laboratory (EMBL) and senior secondary school students from four different classes and their teacher at the Marie-Baum-Schule Heidelberg (MBS).
In order to assess the biodiversity of plants in different habitats within the restored quarry Nussloch, we employed a well-consolidated scientific technology – DNA barcoding. Using this technology, we analysed and compared plants based on their molecular DNA signature. More specifically, our project employed DNA barcoding to assess and compare plant biodiversity in two particular ecological niches in direct proximity: a heavy metal heap on a historical mining site and a rough pasture. The combination of field work with DNA barcoding and the use of modern biological databases providing open-access to DNA sequence data allowed us to increase our understanding of plant biodiversity in these specific ecological niches in the quarry. By successively carrying out all steps of the DNA barcoding process – from plant collection and molecular biology in the laboratory to bioinformatics analysis – the students’ interest in biodiversity-related STEM topics was boosted and raised their awareness of the importance of biodiversity management, particularly in restored mining sites.
Our aim has been to contribute knowledge and data to relevant biological questions relating to quarry biodiversity. The DNA sequence data we generated through our project work has been combined with geolocation data and allows tracking of the plant species identified with smartphone GPS accuracy. For the first time – and as an outcome of our student research project – a compilation of newly generated data sets from biological and geographical sources has been used to establish an online repository cataloguing plant biodiversity in the analysed quarry habitats. This open-access online resource could be extended in the future and might be used for HeidelbergCement’s targeted conservation and restoration approach.
The outcomes of this project are directly fostering the fascination for the uniqueness of quarry habitats. Based on the principle “we can only protect what we know”, our project has further raised public awareness of the importance of biodiversity conservation to safeguard the rich ecosystems in restored quarries.
Students’s activity reports
Introductory session at the Marie-Baum-Schule Heidelberg
Science educators of the European Learning Laboratory for the Life Sciences (ELLS) organised an informative meeting for the group of MBS high-school students to familiarise themselves with the principle of DNA barcoding and to discuss a detailed project plan with them. Supervised by their biotechnology teacher Frank Luft the students will engage in this unique collaboration with the ELLS team and biodiversity experts from HeidelbergCement to assess plant biodiversity in the company’s quarry in Nussloch. The question they hope to answer is related to plants growing on overburden dumps with high levels of heavy metals as they surface in this quarry: Which plant species are able to grow in this environment posing particular challenges to the vegetation? It will be interesting to find out if during evolution distinct (sub)species have evolved that are able to tolerate larger amounts of heavy metals in the substrate they are growing on. Apart from gaining a detailed understanding of plant biodiversity in specific ecological niches of the quarry the team will try to answer additional questions. The whole team is looking forward to collaborate on this exciting project during the coming months and to inform regularly about their progress via the Quarry Life Award website. Stay tuned!
Excursion to the Nussloch quarry – green light for plant collection
On 9 May 2016 our QLA Project began with a field trip to the Nussloch quarry, where we collected as many different plant samples as possible. After school it finally started, we were picked up by the EMBL bus and driven to the quarry in Nussloch. After a short refreshment we received an informative biology lecture on the quarry by Tina Gölzer, an ecologist working at Heidelberg Cement. We then went in teams to work on collecting as many plant species as possible, to document their specific features and to take pictures of them. First we searched on the heavy metal heap and then on the rough pasture. If possible, we tried to find the same plant species in both areas, in order to afterwards analyze them in the EMBL lab. Exhausted after this successful day in the quarry – and full of anticipation for the coming lab day – we made our way home.
Exkursion zum Steinbruch Nussloch – alles im grünen Bereich!
Am 9. Mai 2016 startete die praktische Phase unseres Quarry Life Award Projektes mit einer Exkursion in den Steinbruch Nussloch, um dort möglichst viele verschiedene Pflanzenproben zu sammeln. Nach der Schule ging es endlich los und wir wurden mit dem EMBL-Bus zum Steinbruch nach Nussloch gefahren. Nach einer kurzen Stärkung erhielten wir einen informativen, biologischen Vortrag über den Steinbruch von Frau Tina Gölzer – sie arbeitet als Ökologin bei HeidelbergCement. Anschließend machten wir uns in Teamarbeit an die Aufgabe, in renaturierten Teilen des Steinbruchs möglichst viele verschiedene Pflanzenarten zu sammeln. Jede Pflanzenart wurde von uns fotografiert und die Merkmale in einer Tabelle dokumentiert. Dabei suchten wir zunächst auf einer Schwermetallhalde im westlichen Teil des Steinbruchs und daraufhin auf einer nahegelegenen Magerwiese. Nach Möglichkeit versuchten wir immer, in beiden Habitaten die gleichen Pflanzenarten zu finden, um sie anschließend im EMBL-Labor zu analysieren. Mit vielen in Probenröhrchen verpackten Pflanzen im Gepack, machten wir uns nach dem erfolgreichen Tag erschöpft auf den Heimweg – voller Vorfreude auf den nachfolgend geplanten Labortag.
Exploring the quarry’s DNA in the laboratory
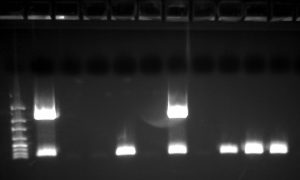
After we had collected various plants for the DNA barcoding at the quarry in Nussloch, we came to the highlight of the project on 13 May 2016: which was the greatly anticipated work in the EMBL laboratory. After a short introduction to the day and a lab safety briefing we started the first wet-lab practicals in the morning. With enthusiasm and in teams of two we set out to extract the DNA from the collected plant samples. Our aim was to amplify specific DNA sequences from the chloroplasts’ genome of the plants by using the polymerase chain reaction (PCR). Small differences in the chloroplast genes allow to genetically discriminate between plant species – or even sub-species. On this day we concentrated on the rbcL gene. After we refreshed ourselves in the EMBL Cafeteria, we returned to the lab to separate the amplified DNA fragments through gel electrophoresis – a standard molecular biology procedure to visualize DNA of certain length. Each of us was concentrating on correctly pipetting the amplified DNA fragments onto the gel. Then we watched with great anticipation as to whether our efforts and commitment had paid off. Some results were very promising, others were a bit puzzling. But all in all the results were satisfactory and we sent the DNA off for sequencing to read out the genetic information and to be able to analyse it during the upcoming bioinformatics session.
Die DNA des Steinbruchs
Nachdem wir am 9. Mai 2016 im Steinbruch in Nussloch diverse Pflanzen für das DNA-Barcoding gesammelt hatten, stand am 13. Mai 2016 das absolute Highlight des Projektes an, nämlich die mit voller Vorfreude erwartete Arbeit in den Laboren des EMBL. Um 10:00 Uhr stand nach einer kurzen Einführung und Laborsicherheitsbelehrung der erste Laborteil auf dem Plan. Mit Begeisterung machten wir uns in Zweiergruppen daran, zunächst die DNA aus den gesammelten Pflanzenteilen zu extrahieren. Unser Ziel war es, ganz bestimmte DNA bzw. Genabschnitte aus dem Chloroplasten-Genom der Pflanzen mittels der Polymerase-Ketten-Reaktion (PCR) zu vervielfältigen. Kleine Unterschiede in den Genen der Chloroplasten erlauben es nämlich, die Pflanzen genetisch einer Art oder sogar Unterart zuzuordnen. Wir konzentrierten uns an diesem Tag auf die rbcL-Fragmente (große Untereinheit des Ribulose-bisphosphat- carboxylase Gens). Nachdem wir uns in der EMBL-Kantine gestärkt hatten, ging es wieder ins Labor, um die in der PCR vervielfältigten Fragmente durch ein Agarosegel elektrophoretisch aufzutrennen. Mit Konzentration war jeder von uns damit beschäftigt, die gewonnene DNA unversehrt in die Taschen des Gels zu pipettieren. Anschließend beobachteten wir mit großer (An-) Spannung, ob sich unser Bemühen und Engagement gelohnt hatte. Einige Ergebnisse waren sehr vielversprechend, andere wiederum zunächst etwas rätselhaft für uns. Doch alles in allem waren die Resultate zufriedenstellend und wir schickten die DNA zur Sequenzierung, um die darin enthaltene Erbinformation auszulesen und sie dann später bioinformatisch bearbeiten zu können.
Bioinformatics analysis workshop – the key to species identification
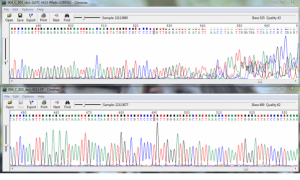
The next step in our Quarry Life Award Project was waiting for us on the 2nd of June 2016: the bioinformatics analysis of our plant samples. Meeting at the computer lab of the Marie-Baum-Schule in Heidelberg, we started off with a short review of the lab work we had carried out previously at EMBL. As some of us are still in grade 11 and not yet familiar with the theory of molecular methods such as PCR, we discussed the theoretical basis of this method in greater detail before going on to look at the promising results of our gel electrophoresis. Then, the most important part of the day started: the analysis and interpretation of our DNA sequences. As we had asked the sequencing service to “read” our DNA sequence from both ends, we received two complementary sequences for each PCR product from them. To be able to compare the two, we first used a bioinformatics tool to translate one of the two reads into its reverse complement. We then went on to compare the two reads base by base, resolving any mismatches between them. The final step of the bioinformatics analysis involved searching for a match of our, now error-corrected, DNA sequence (contig) with entries in a biological database (European Nucleotide Archive). After discussing the theory and taking on analysing our real DNA sequences, we all left the session with new knowledge and a great sense of achievement.
Bioinformatik – der Schlüssel zur Artenbestimmung
Am 2. Juni 2016 kamen wir zum nächsten Schritt unseres Quarry Life Award Projektes. Dies war der bioinformatische Teil zur Bestimmung der verschiedenen Pflanzenproben. In einem der Computerräume unserer Marie-Baum-Schule in Heidelberg begannen wir mit einer kurzen Wiederholung der Arbeiten bei unserem Laboreinsatz am EMBL. Da manche von uns noch die 11. Klasse besuchen und sich deshalb mit der Methode der PCR noch nicht so gut auskannten, wurde diese noch einmal ausführlich erklärt, sodass nun alle von uns auf dem gleichen Wissenstand waren. Anschließend besprachen wir die Gelelektrophorese, die bereits einige positive Ergebnisse angezeigt hatte. Dann folgte der wichtigste Teil des Tages – die bioinformatische Auswertung der Sequenzen. Da bei der Sequenzierung beide DNA-Stränge „gelesen“ werden, erhält man zwei komplementäre Sequenzen pro PCR-Produkt. Um diese zu vergleichen, muss zunächst eine der beiden Sequenzen „umgekehrt“ werden (revers komplementär). Nun können die Sequenzen beider DNA-Stränge Baustein für Baustein miteinander verglichen werden. Dies geschieht um unklare Sequenzbereiche zu klären. Durch Abgleich der DNA-Sequenz mit einer biologischen Datenbank (European Nucleotide Archive) kann man nun mit der korrekturgelesenen Sequenz (Contig) die Artenbestimmung durchführen. Nach der Theorie kam die Praxis und wir haben anhand von Beispielen das ganze Verfahren erfolgreich getestet. Somit gingen wir alle mit neuem Wissen und einem Erfolgserlebnis nach Hause.
Visit of the International Jury of the Quarry Life Award 2016
On the 21st July 2016 we had the honour to present our project updates to Professor Rademacher. He is member of the International Jury of the Quarry Life Award 2016, and on this day we met him at EMBL Heidelberg. Our team had prepared everything in advance and were looking forward to present the project. After welcoming our guest, we gave a talk about our project, answered Professor Rademacher’s questions on the methods that we have used and talked about our experiences as participants of the award. We received very positive feedback on our presentation by Professor Rademacher, which we were, of course, happy to hear. After a short coffee break, in which our guest further discussed the project with us, we went to the laboratory. In the lab, we showed him the individual experimental steps involved in DNA barcoding, which we had carried out so far. After presenting our guest with a “Barcode-Sunflower” gift and taking a group picture, it was time to say goodbye. We would like to sincerely thank Professor Rademacher for his interest in the project and the many tips we received from him. “We hope you enjoyed it as much as we did.”
Besuch der International Jury des Quarry Life Award 2016
Am 21. Juli 2016 hatten wir die Ehre, den Stand unseres QLA-Projekts Herrn Professor Rademacher vorzustellen. Er ist Mitglied der internationalen Jury des Quarry Life Award 2016 und wir trafen ihn an diesem Tag am EMBL Heidelberg. Als Team hatten wir im Vorfeld bereits alles vorbereitet und freuten uns auf die Projektvorstellung . Nach einer Begrüßung unseres Gastes präsentierten wir unser Projekt zunächst in einem Vortrag, beantworteten seine inhaltlichen Fragen zu unserem methodischen Vorgehen und sprachen auch über unsere Erfahrungen und Erlebnisse bei der Teilnahme am Wettbewerb. Für unsere Präsentation bekamen wir sehr positives Feedback von Herrn Rademacher, über welches wir uns natürlich sehr gefreut haben. Nach einer kurzen Kaffeepause, in der sich Professor Rademacher weiter angeregt mit uns unterhielt und uns weitere Fragen über unser Projekt stellte, ging es ins Labor. Dort zeigten wir ihm die verschiedenen experimentellen Arbeitsschritte des DNA Barcoding, wie wir sie bereits durchgeführt hatten. Nach der Übergabe unserer „Barcode–Sonnenblume“ und einem gemeinsamen Gruppenfoto, endete dieser Einblick in den momentanen Stand unserer Projektarbeit. Wir möchten uns noch einmal sehr herzlich bei Professor Rademacher für sein Interesse an unserem Projekt und die zahlreichen Tipps bedanken. „Wir hoffen es hat Ihnen genau so viel Freude bereitet wie uns.“
Visit of the National Jury of the Quarry Life Award 2016
We were pleased to welcome Ms. Christiane Bohlmann, Head of Marketing at HeidelbergCement Germany and member of the National QLA Jury, on the 15th September 2016. She visited us in the Advanced Training Centre at EMBL to learn more about the up-to-date status of our QLA project. First, we presented an overview of our project “Quarry biodiversity in focus – exploring the barcode of life”. She showed great interest and we were very happy to answer all her questions. Before going to the laboratory, we had a short coffee break, which Ms. Bohlmann used to further quiz us about the project and tell us about her experiences when visiting other project presentations. In the lab, we presented and discussed the various experimental steps involved in DNA barcoding. The visit ended with presenting our guest with a “Barcode-Flower” gift and taking a group picture in the sunshine outside. We would like to sincerely thank Ms. Bohlmann for her interest in our project and hope she found the visit as enjoyable as we did.
Besuch der Nationalen Jury des Quarry Life Award 2016
Mit Frau Christiane Bohlmann, Leiterin des Marketings von HeidelbergCement Deutschland, konnten wir am 15. September 2016 ein Mitglied der nationalen Jury des Quarry Life Award begrüßen. Sie stattete uns im Advanced Training Center des EMBL einen Besuch ab, um mehr über den Stand unseres QLA-Projektes zu erfahren. Zunächst einmal präsentierten wir Frau Bohlmann eine Übersicht über unser Projekt „Die Biodiversität von Abbaustätten im Fokus – dem Barcode des Lebens auf der Spur“. Wir freuten uns sehr, dass Sie nach dem Vortrag viele interessierte Fragen stellte, die wir ihr gerne beantworteten. Bevor wir zusammen ins Labor gingen, legten wir eine kleine Kaffeepause ein, bei der wir uns weiter angeregt unterhielten und Frau Bohlmann uns auch von ihren Erlebnissen bei anderen Projektvorstellungen erzählte. Im Labor stellten wir unserem Gast die verschiedenen experimentellen Arbeitsschritte des DNA Barcoding vor und erklärten diese. Nach dem Überreichen unserer “Barcode-Blume” gingen wir nach draußen, um bei schönstem Wetter ein gemeinsames Gruppenbild zu machen und so den Einblick in unsere Projektarbeit zu beenden. Wir bedanken uns herzlichst bei Frau Bohlmann für Ihr Interesse an unserem Projekt und hoffen es hat ihr genauso viel Spaß gemacht wie uns!
Project key dates
Project coordinator: ELLS
Funding: Quarry Life Award, HeidelbergCement
Duration: 5 months
Start: 05/2016
End: 09/2016